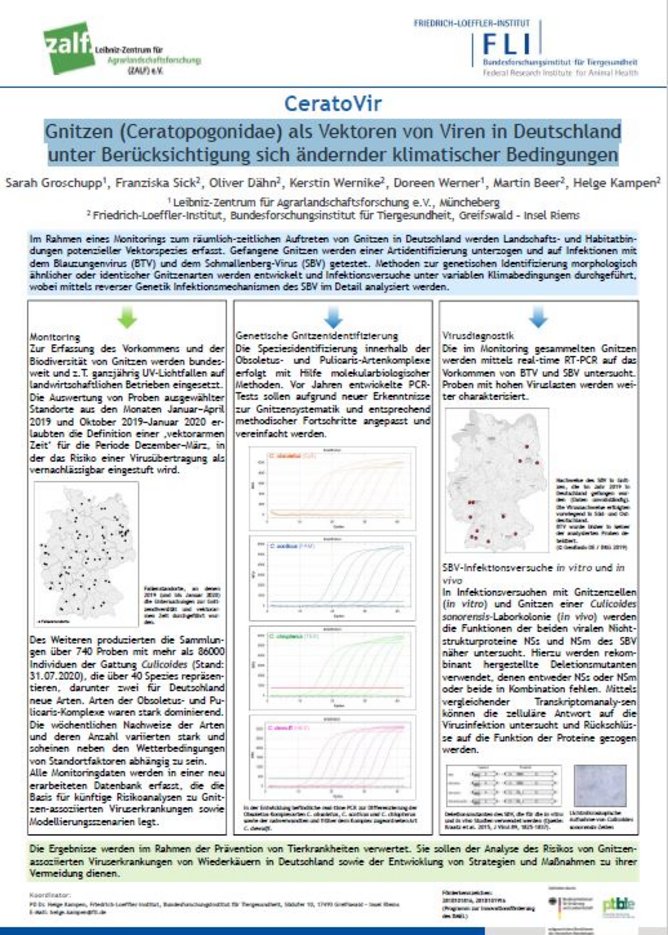
Obwohl aus dem Monitoring bisher im Wesentlichen nur regionale Daten aus limitierten Zeiträumen vorliegen, scheint die Gnitzenaktivität in Deutschland sowohl saisonal länger als auch in den Frühjahrs- und Herbstmonaten intensiver zu sein als noch in den Zeitperioden des ersten BTV- (2007-2009) und des ersten SBV-Ausbruchs (2011-2013). Auf Grundlage dieser Daten konnte eine „vektorfreie/-arme Zeit“ im Winter vorgeschlagen werden, in der die Gnitzenaktivität unter einen festgelegten Schwellenwert fällt und daher Lockerungen von Handelsbeschränkungen mit Wiederkäuern aus einer Blauzungen-Restriktionszone möglich sind. Zudem erbrachte die bisherige Datenauswertung das Vorkommen zweier neuer Gnitzenarten für Deutschland.
Bei der Entwicklung der Tests zur genetischen Artidentifizierung der Gnitzen stehen die Arten des Obsoletus- und Pulicaris-Komplexes im Fokus. Für den Obsoletus-Komplex wird derzeit eine quantitative und multiplexfähige realtime PCR als Methode entwickelt, die eine zuverlässige Identifizierung der Komplexarten C. obsoletus, C. scoticus und C. chiopterus sowie der nahverwandten Art C. dewulfi ermöglichen soll. Parallel wird eine konventionelle PCR für den Pulicaris-Komplex entwickelt, die alle potenziellen Vektorarten dieses Komplexes identifizieren soll.
Das Virus-Screening von im Monitoring 2019 gesammelten Gnitzen ergab mehrere SBV-Nachweise, vorwiegend in Ost-und Süddeutschland. Der saisonal früheste Nachweis gelang in Ende April 2019 gesammelten Gnitzen. BTV wurde bisher nicht detektiert. Die Ergebnisse spiegeln wider, dass SBV im Jahr 2019 häufig im Säugetierwirt (= Wiederkäuer) auftrat, während BTV in Wiederkäuern kaum nachgewiesen wurde.
Für Infektionsversuche konnte eine Culicoides sonorensis-Kolonie am FLI etabliert werden. In vivo-Infektionsversuche mit unterschiedlichen Virusstämmen dauern an. Um die Funktion viraler Proteine im Insektenvektor näher zu bestimmen, werden in vitro-Infektionsversuche mit rekombinant hergestellten SBV-Deletionsmutanten im Gnitzen-Zellkultursystem durchgeführt. Mittels vergleichender Transkriptomanalysen wird die zelluläre Antwort auf die Virusinfektion untersucht.